近年来基于主链骨架等级基础上的通过诱导和维护螺旋结构的人造螺旋聚合高分子实用性分子设计方法论的研究
- 2013-02-18
- 专题
 1.简介
1.简介
1-1.螺旋聚合物的短暂历史1a,b
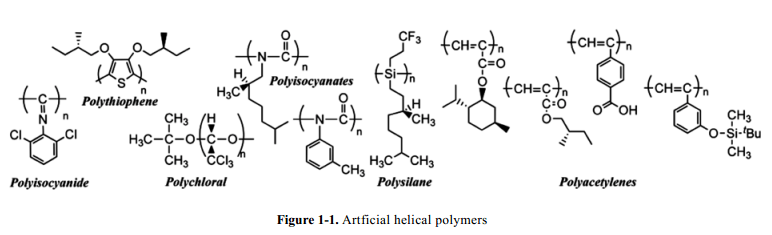
螺旋结构高分子化合物的研究几乎与聚合物的独立类型研究,即蛋白质螺旋结构(Pauling, 1951)、DNA双螺旋结构(Watson, Crick, 1953)以及等规聚丙烯1/3-螺旋结的构澄清开始于同一时间。尤其是,Natta发现了等规聚丙烯具有一个先进的技术,意味着聚合物螺旋结构可以通过良好的合成反应对在聚合物结构设计中立体规则性以及相应的单体的微控人工构造出来。随后,合成具有庞大的取代基的螺旋聚合物构型被研究出来,从而可以生成了这种聚合物的各种类型例如聚异氰酸酯,2a,b聚异氰化合物,3 聚醛,4聚(烷基异丁烯酸酯),5 聚硅烷,6 聚乙烯,7a-d 聚噻吩8(Fig. 1-1)。这些刚性与半刚性聚合物主链可以用来解释维护聚合物的螺旋构象。
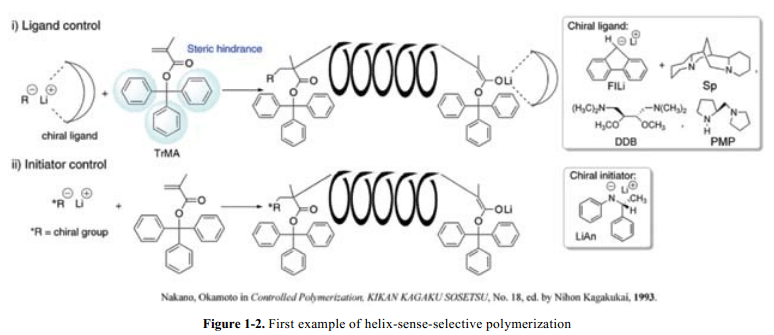
合成螺旋聚合物作为一个显著的工作,Okamoto和他的伙伴报道了丙烯酸酯的不对称聚合。5在这个聚合系统里面,螺旋构象的螺旋性质通过由加成聚合物引发剂组成的手性不对称配合基控制。通常,具有灵活主链骨架的聚合物在溶液里面不能够维持其螺旋构象,因为聚合物主链旋转没有强大的约束。因此,为了维护聚合物螺旋构象,精确的使用它们的空间位阻现象引入巨大的侧链可以制作高分子聚合物主链。例如,聚(甲基丙烯酸三苯甲酯) 显示稳定的螺旋构象(Fig. 1-2), 与聚(甲基丙烯酸甲酯)在溶解态中的无规则的卷曲状形成鲜明的对比。在一个自然的结果中,聚合物主链绕线方向的测定意味着聚合物螺旋构象螺旋意义的确定。由乙烯基单体制得的合成高分子具有sp3-碳循环序列组成的聚合物主链。因此这种类型的螺旋聚合物,他们没有有效的需要足够的范德华力的互相间作用的官能团来维持螺旋构象。相反的,生物聚合物例如多肽就通过氢键和范德华力共同引导和维持其螺旋构象。尤其是,分子内和分子间的氢键促成了聚合物二级结构的形成。然而,在合成聚合物中合适的氢键序列很难构建。因此,除了合成DNA 或者多肽,其他的鲜有报道。
1-2. 近期研究的综述
光学活性聚合物研究在合成方面可以大致分为两种类型:重复单元有手性中心的和没有手性中心的。前者一个例子,聚合物主链上引入单体分子不对称中心式最常用的方法,比如光学活性单体聚合通过联萘为代表 (Habaue–Okamoto9,Tsubaki10)。除此之外,综合方法目前承担着对于主链上重复单元手性控制,即手性单体不对称聚合螺旋状选择性类型(Okamoto11, Nozaki12)和 外消旋单体聚合不对称单体选择性类型(Kakuchi13)。另一方面,后者方法的处理,原子群各向异性排列感应现象,也就是,借助于单体内部或者外部不对称源半刚性主链所产生的螺旋构象的手性和稳定性都会试图以聚乙炔和聚异氰酸酯螺旋状选择性聚合作用为代表。根据聚合物主链基本结构,这些具有轴向手性诱导(没有手性原子)光学活性聚合物在聚合物主链上粗略分为sp3–sp3型和sp2–sp2型。此外,sp2–sp2类型聚合主链光学活性聚合物更进一步的分为共轭和交叉共轭主链聚合物(Fig. 1-3)。
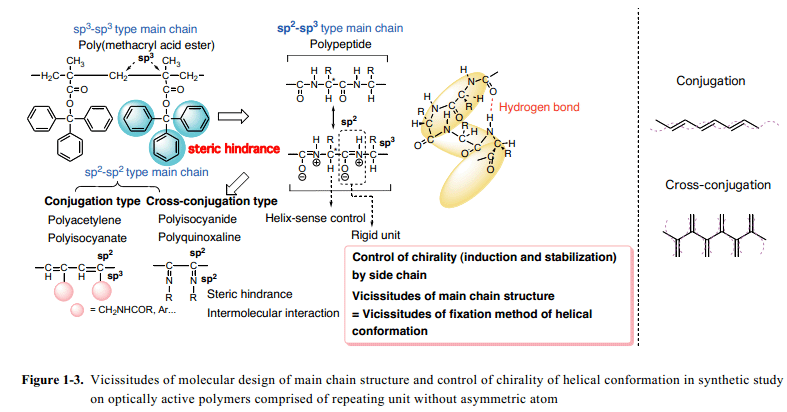
上面所述的早期的螺旋高分子聚丙烯酸酯归类为一种具有sp3–sp3主链的螺旋聚合物,其构象的稳定性很大程度上取决于酯部分中的烷基基团。烷基取代导致了螺旋结构稳定性上很大程度的差异。尽管多肽本质上归类为sp3–sp2型主链聚合物,120˚键角肽键的平面性质归因于共振酰胺部分提供部分刚性聚合物结构的聚合特征。α–螺旋构象的螺旋性质由α-碳和强力稳定构象的分子内氢键而决定的。后来光学活性聚合物的发展趋势已经转移到处理具有sp2–spa(a=2,3)类型主链重复单元的聚合物上面。聚乙炔和聚异氰酸酯都是具有共轭sp2–sp2 类型主链特征的聚合物,其中侧链键通过sp2–sp3 键合诱导,稳固手性特征。另一方面,聚异氰化物是具有交叉共轭sp2–sp2 型主链结构的聚合物,其中侧链键通过sp2–sp2 键合控制手性特征。对于这种类型的聚合物的合成,各种共轭与非共轭立体控制技术被研究出来。这种类型的光学活性聚合物获得很大的收益,并且各种控制技术被提出和研究,尤其是从人造聚合物螺旋构象的设计和合成为出发点。
2. 螺旋结构的诱导和稳定性
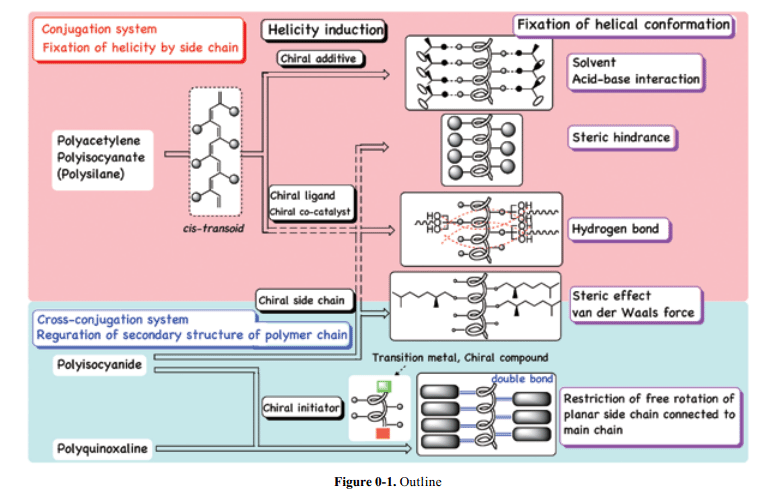
本文介绍了近期合成人造螺旋聚合物的研究工作,聚焦这些在重复单元出既无对称中心业务对称轴心的螺旋聚合物,根据合成方法可以分为三种类别:1)固定或者稳定的螺旋结构;2)分子外围分子不对称因素诱导的高分子主链构象;3)分子内不对称因素不对称诱导的高分子主链构象。
2-1. 用于聚合物螺旋构象的固定方法
本节讨论用于维持聚合物螺旋结构与螺旋选择性高分子螺旋构象的实用方法。这个目标的合成方法如下:1)分子间主-客体相互作用;2)金属离子的配位或螯合;3)范德华力(相互作用);4)酸碱相互作用;5)氢键结合;6)庞大的侧基立体效应等。
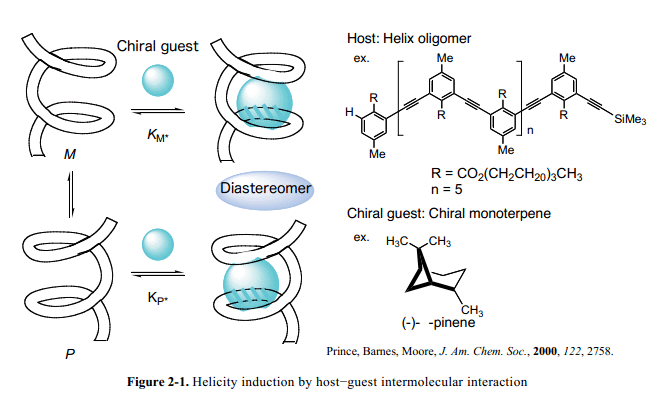
Moore 和他的伙伴们报道了m-苯乙炔撑低聚物的固定的螺旋构象(作为主体)通过手性单萜(作为客体)在乙腈溶液中以1:1混合比例而形成(Fig. 2-1)。14Inouye和他的同事已经揭示了聚(m-乙炔基吡啶)(作为主体)螺旋构象的电磁感应通过氢键和糖模板实现。15在这个系统里面,螺旋构象通过分子间氢键和刚性主链结构来固定。
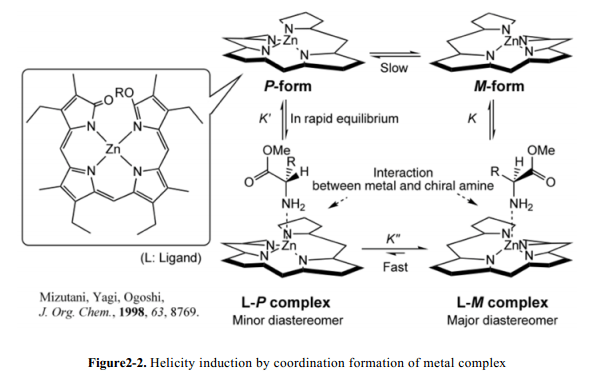
Ogoshi和同事16,Shinkai和其同事17 已经实现了感应芳香烃化合物螺旋构象,通过Zn或者Cu的螯合和手性添加剂分子分子间相互作用固定螺旋意义上的螺旋构象的(Fig. 2-2)。螺旋意义上的螺旋取决于更多的手性分子的结构。此外,Ishimaru和其同事保留了卟啉二聚体螺旋意义的螺旋构象诱导如下:外消旋卟啉二聚体与Zn(II)配合,借助手性胺-Zn相互作用由手性胺处理诱导螺旋构象,随后移除手性胺,Ba2+离子与冠醚配合。18
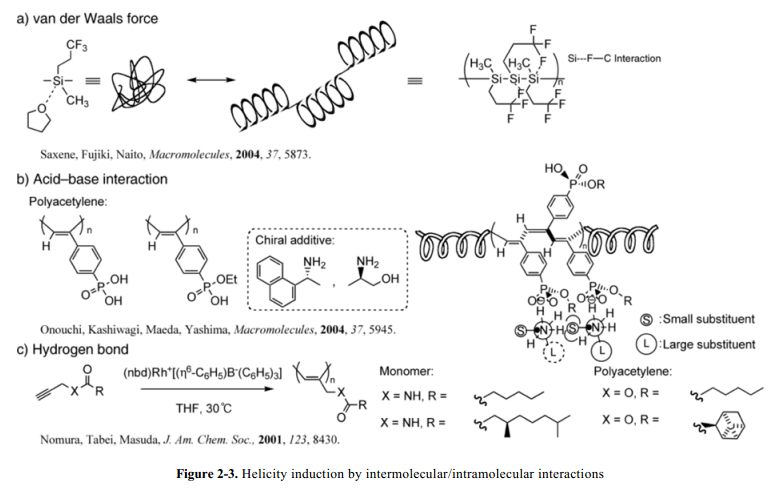
Fujiki 和其同事借助于Wurtz coupling 成功的合成了二甲硅同系物。这个聚硅烷具有长的烷基链,末端连接三氟甲基,通过微弱的Si---F–C间作用诱导和维护其螺旋构象。他们打算开发利用这种微弱的分子间范德华力的功能性材料。这个工作后来在Topic 1详细描述:手性研究转移和扩增。19
Yashima、Okamoto和他们的同事已经实现了聚乙炔衍生物(含有羧酸基侧链或者磷酸部分的)的螺旋主链构象的诱导和维护。他们利用高分子主链上酸性侧基和手性胺添加剂之间的酸碱作用诱导螺旋构象的感应现象,并且证明了手性醇替换手性胺之后其构象螺旋感应现象仍然保留。这项工作被后面的Topic 2详细描述:手性记忆。
Masuda和他的同事通过借助于侧链之间的氢键报道了poly(N-propargylamide)(具有笨重的手性侧链和螺旋构象的顺反结构的螺旋构象的)的诱导作用(Fig. 2-3c)。21
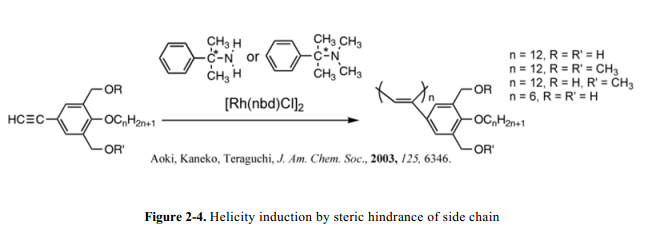
Aoki 和他的同事们清楚的演示了对比上述研究所不同的方法。由Yashima’s团队和Masuda’s团队报道了具有螺旋结构的聚合物的合成,其中手性醇和手性侧链的存在是维护螺旋构象不可或缺的。相反,Aoki和他的同事证明了高分子聚合物(不使用不对称源除了手性助催化剂(R)-/(S)-phenylethylamine)螺旋构象感应现象的维护(Fig. 2-4)。22,23这归因于单分子结构队列合适的设计,其中相应单元的氢键作用和大体积侧基大致功能最为有效。
2-2.利用分子外不对称源的不对称诱导作用
在本节中,在重复单元主链或者侧链部分没有不对称因素的高分子聚合物螺旋构象的不对称诱导现象被具体描述。这种感应通过借助于单体或者聚合物分子外在的不对称因素来进行完成。
Green 和他的同事们报道了poly(hexylisocyanate)由于其螺旋构象的原因在手性氯烷烃溶剂中显示出一种Cotton效应。Yamashita和他的同事们报道了螺旋构象借助于手性添加剂和聚合物极性侧链间的分子间相互作用的一个成功的诱导。例如,polyisocyanide的螺旋构象的诱导作用通过手性胺和hydroxycarbonyl侧链间的酸碱作用来完成25,poly(phenylacetylene)的手性添加剂 分子通过冠醚侧链实现虏获。26基于这种方法的一个应用,他们展示了制备高分子电解质螺旋构象的方法。27
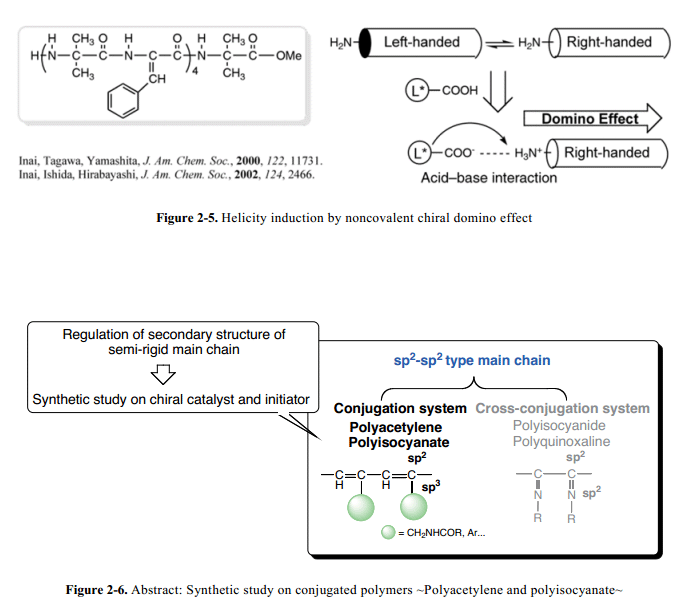
Fujiki和他的同事们报道了polysilane 通过添加手性醇的螺旋构象诱导效应的进行。28 此外,Masuda和他的同事们报道了手性N-propargylamide 通过酰胺侧基和手性醇或者胺分子添加物之间的氢键作用的螺旋构象的诱导效应。1bInai和他的同事们发现整个多肽链的螺旋感应简单的通过多肽的N-末端和依赖手性羧酸绝对构象的手性羧酸添加物之间的酸碱作用诱导(多米诺效应) (Fig. 2–5)。29
另一方面,有几个不使用手性添加剂或者手性溶剂观测到螺旋诱导现象的例子。Okamoto和他的同事们报道了聚噻吩借助于甲醇或者Cu(II)离子添加物实现了其不对称诱导, 在良好的溶剂比如CHCl3中显示无诱导CD。30
这个延伸到开发具有切换功能的手性超分子的研究中。为了实现开闭作用,发现了聚噻吩,在氯仿-乙腈混合溶液中,参杂Cu(II)–联吡啶络合物被利用。
在开发新型手性催化剂和引发剂的基础上,有大量的工作从事于催化剂或引发剂的选择上面,他们根据产物聚合物主链组合的灵活调整和单体庞大的侧链来进行选择。聚乙炔和聚异氰酸酯的手性特征的控制通过侧基单键以sp2–sp3形式链接在共轭聚合物主链上(Fig. 2–6)。因此,已经有研究将用来开发手性催化剂控制聚合物主链构象。
由Rh或Mo组成的过渡金属络合物催化剂被用于控制聚乙炔主链构象。尤其是,[(nbd)RhCl]2和MoOCl4–nBu4Sn已经被认为是用于cis-transoid构象感应的有效催化剂。Noyori和其同事已经发现,Rh+(diene)[(η6-C6H5)B-(C6H5)3]类两极离子Rh(I)络合物的二烯配体很大程度上影响高分子聚合作用反应性。32此外,他们已经借助于Rh+(nbd)[(η6-C6H5)B-(C6H5)3]引发剂从含有长的烷基侧链的单体中成功的合成了具有螺旋构象感应的聚乙炔(Fig.2-7,left)。这个含有自由的卤素原子引发剂,温和的反应条件下可以担负高分子量的聚合物使得反应温度低于室温。另一方面,Okamoto和其同事报道了阴离子引发剂比如(-)-薄荷醇锂盐或 (S)-(+)-2-(1-吡咯烷甲基)吡咯烷能够负担芳香聚异氰酸酯的螺旋构象螺旋screw-sense(Fig. 2-7, right)。2b
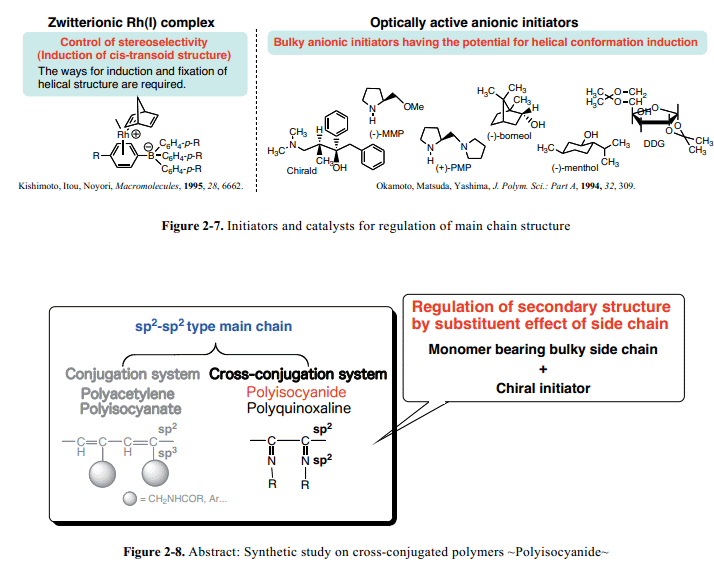
聚异氰化物和聚喹喔啉被列为交叉共轭主链聚合物。聚异氰化物螺旋构象screw-sense的控制与调节本质上取决于侧基通过双键形式(sp2–sp2)链接到主链上。单体取代基效应在手性引发剂研究过程中唤起了人们极大的兴趣(Fig. 2-8)。
Nolte和其同事通过处理含有(R)-(+)-/(S)-(-)-(1-苯乙基)甲胺和镍(II)四(叔丁基异腈)组成的引发剂大取代基的非手性异氰化物,成功的选择性合成了聚异氰化物螺旋构象screw-sense。3
另一方面,Takahashi 和其同事借助于铂–钯双核络合物催化剂和低聚物引发剂实现了聚异腈(从手性和非手性异氰化物而来的)的screw-sense螺旋构象(Fig. 2-9)。33 这个高分子共聚物具有同样的螺旋结构screw sense链接手性单体同聚物。着这个系统里面, 存在的无规共聚物按低聚物顺序排好是必不可少的,在这里,手性单体通过类似Sergeants和Soldiers rule的热力学控制来管理螺旋screw-sense。在本质上类型相同,Drenth和其同事完成了聚异腈的合成以及通过非手性异腈和具有大的侧链的手性异氰化物的共聚作用聚合物的螺旋构象screw-sense感应。34然而,其螺旋screw-sense与单独自含有手性侧链单体合成而来的均聚物正好相反(Fig. 2-10, left)。这个出乎意料的结果被理解如下:非手性异氰化物聚合得到大量的右旋和左旋screw-sense螺旋聚合物,导致螺旋聚合物外消旋混合物(聚合物)的形成。另一方面,光学活性(手性)异氰化物单体的聚合作用仅仅担负两个螺旋构象screw-sense的一个。
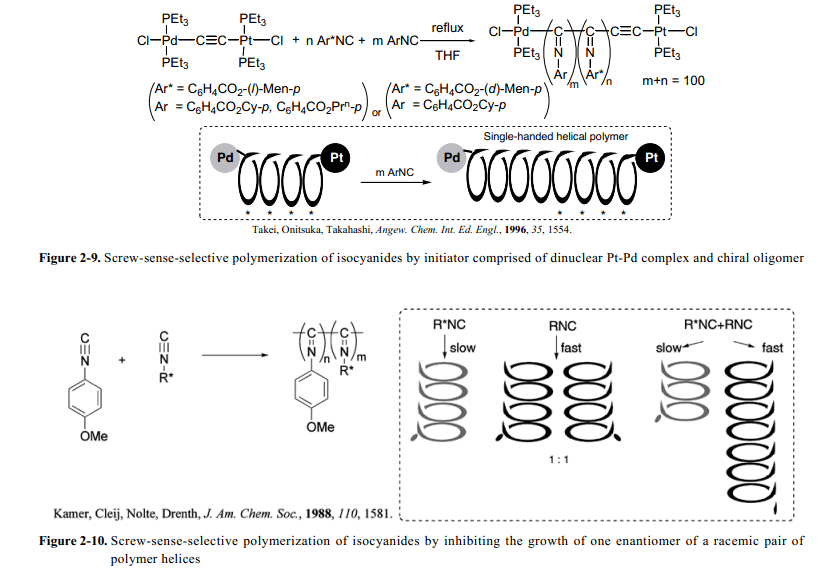
此外,光学活性异氰化物单体的聚合作用慢于非手性氰化物。其中聚合蔓延的速度非常慢的手性单体能够影响到由非手性异氰化物单体而来的螺旋聚合物末端蔓延。然而,手性异腈单体在由非手性异腈单体衍生得到的两种螺旋聚合物中反应速率的差异是很重要的,它只允许非手性异腈单体螺旋聚合物末端的反应,手性异腈单体所承担的与螺旋方向一致。此外,高分子链末端链接的手性异腈单体很容易抵制下面的反应。与这种情况是一致的,螺旋高分子的两种screw-sense中的一个收到很强大的控制可以允许螺旋高分子另外一个screw-sense的高分子聚合终端反应优先形成螺旋聚合物的screw-sense(Fig. 2-10, right)。
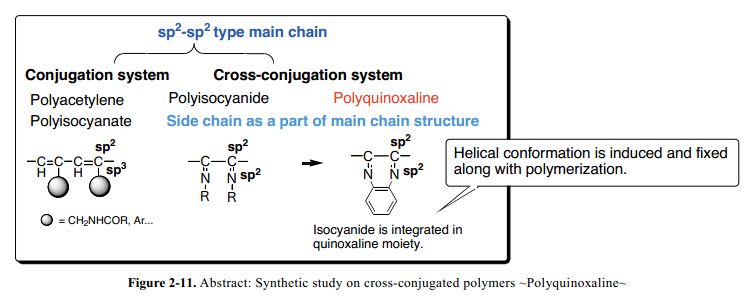
与螺旋聚异氰化物聚合物支柱screw-sense通过侧链“独立”控制和管理相反, C=N键对并入喹喔啉杂芳环形式延伸的侧链可以有效的修复聚合物链。一个自然的结果中,利用喹喔啉单元的如此的特点已经开发了一系列的螺旋聚合物, 并入聚合物主链然后沿着螺旋构象感应进行主链的延伸(Fig. 2-11)。
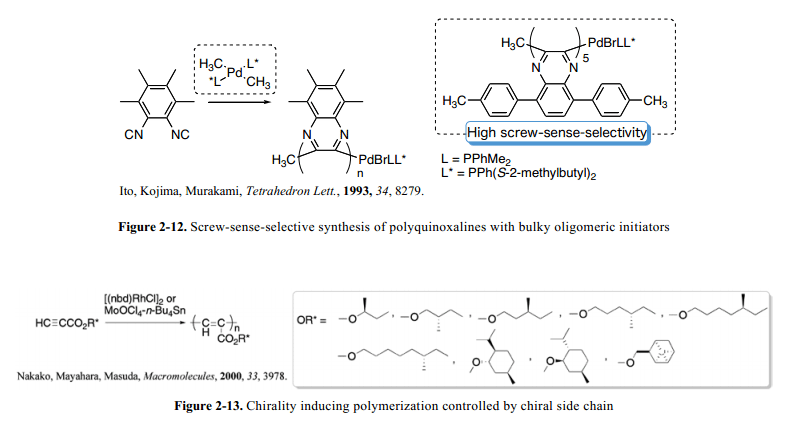
Ito和其同事报道了1,2-diisocyanoarenes借助于Pd(II)复合物的高分子聚合。35 他们报道在具有相对低选择性手性膦配体的Pd(II) 复合物帮助下用于螺旋结构screw-sense的产生,相对于获得的聚喹喔36,借助于光学喹喔啉pentamer-Pd(II) 复合物可以高选择性的实现螺旋screw-sense(Fig. 2-12)。37 此外,基于分离检查的基础上,我们发现screw-sense-selectivity的实现并不取决于膦配体的取代基类型。36这就意味着,Pd(II)复合物螺旋screw-sense的选择性不是决定于膦配体的手性特征,而是决定于聚合物的二级结构。这样的考虑基础上,Suginome和其同事借助于含有简单不对称源1,1'-联萘的Pd(II)复合物成功的完成了1,2-diisocyano-3,6-di-p-toluoylbenzene的螺旋screw-sense-selective聚合作用。38 这个screw-sense-selective螺旋结构成功的感应现象归因于先前形成的引发剂螺旋构象本身具有很高的screw-sense-selectivity。因此,联萘核心取代基的选择决定了聚合作用中螺旋构象的screw-sense-selectivity。
2-3. 利用分子内部不对称源的螺旋Screw-Sense 感应现象
在本节中,将会介绍一些借助于单体内不对称源的螺旋screw-sense感应。关于这一类的方法,具有手性侧链的单体的简单聚合作用和由手性侧基控制的特定环境下的聚合作用比如分子间相互租用或者侧基间空间排斥都有报道。Masuda 和其同事合成了一系列具有不同长度手性侧链或者大小的聚乙炔
参考文献
1) (a) R. Nomura, J. Tabei, T. Masuda, Macromolecules 2002, 35 , 2955-2961. (b) J. Tabei, R. Nomura, F. Sanda, T. Masuda, Macromolecules 2003, 36, 8603-8608.
2) (a) M. Green, C. Andrea, M. Reidy, J. Am. Chem. Soc. 1988, 110, 4063-4065. (b) Y. Okamoto, M. Matsuda, E. Yashima, J. Polymer Science: Part A 1994, 32 , 309-315.
3) P. Kamer, R. Nolte, W. Drenth, J. Am. Chem. Soc. 1988, 110, 6818-6825.
4) K. Ute, K. Hirose, K. Hatada, J. Am. Chem. Soc. 1991, 113, 6305-6306.
5) T. Nakano, Y. Okamoto, KIKAN KAGAKU SOSETSU 1993,18,129.
6) M. Fujiki, High POLYMERS 2004, 53 , 938-941.
7) (a) H. Nakako, R. Nomura, T. Masuda, Macromolecule, 1999, 32, 2861-2864. (b) H. Nakako, Y. Mayahara, T. Masuda, Macromolecules 2000, 33, 3978-3982.(c)E. Yashima,T.Matsushima,Y.Okamoto, J.Am. Chem. Soc. 1997, 119, 6345-6359. (d) E. Yashima, S. Huang, Y. Okamoto, Macromolecules 1995, 28 , 4184-4193.
8) B. Langeveld-Voss, E. Meijer, J. Am. Chem. Soc. 1996, 118, 4908-4909.
9) S. Habaue, T. Seko, Y. Okamoto, Macromolecules 2003, 36,2604-2608.
10) K. Tsubaki, M.Miura,H.Morikawa,J.Am. Chem. Soc. 2003, 125, 16200-16201.
11) (a)T. Nakano, K. Tsunematsu, Y. Okamoto, Chem. Lett. 2002, 31 , 42-43. (b) N. Hoshikawa, Y. Hotta, Y. Okamoto, J. Am. Chem. Soc. 2003, 125, 12380-12381.
12) K. Nozaki, J. Polymer Science: Part A 2004, 42 , 215-221.
13) M. Tsuji, R. Sakai, T. Kakuchi, Macromolecules 2002, 35 , 8255-8257.
14)R. Prince, S. Barnes, J. Moore, J. Am. Chem. Soc. 2000, 122, 2758-2762.
15) M. Inouye, M. Waki, H. Abe, J. Am. Chem. Soc. 2004, 126, 2022-2027.
16)(a) T. Mizutani, S. Yagi, H. Ogoshi, J.Org. Chem. 1998, 63, 8769-8784. (b) T. Mizutani, S. Yagi, H. Ogoshi, J. Org. Chem. 1998, 63 , 8769-8784.
17)M. Yamamoto, M. Takeuchi, S. Shinkai, J. Chem. Soc. Perkin Trans. 2 2000, 9-16.
18)Y.Kudo, T. Ohno, Y. Ishimaru, J. Am. Chem. Soc. 2001, 123, 12700-12701.
19) A. Sexana, M. Fujiki, M. Naito, Macromolecules 2004, 37 , 5873-5879.
20)a) E.Yashima,K.Maeda,Y.Okamoto,Nature 1999, 399, 449-451. b) H. Onouchi,D. Kashiwagi, K. Maeda, E. Yashima, Macromolecules 2004, 37 , 5495-5503.
21) R. Nomura, J. Tabei, T. Masuda, J. Am. Chem. Soc. 2001, 123, 8430-8431.
22) T.Aoki, T. Kaneko,M.Teraguchi, J. Am. Chem. Soc. 2003, 125, 6346-6347.
23) Y. Umeda, T. Kaneko, M. Teraguchi, T. Aoki, Chem. Lett. 2005, 34 , 854-855.
24) M. Green, C. Khanti, C. Peterson, J. Am. Chem. Soc. 1993, 115, 4941-4942.
25) M. Ishikawa, K. Maeda, E. Yashima, J. Am. Chem. Soc. 2002, 124, 7448-7458.
26) R. Nonokawa, E. Yashima, J. Am. Chem. Soc. 2003, 125, 1278-1283.
27) H. Onouchi, K. Maeda, E. Yashima, J. Am. Chem. Soc. 2001, 123, 7441-7442.
28)H.Nakashima,J.Koe, K.Torimitsu,M.Fujiki, J.Am.Chem.Soc.2001,123, 4847-4848.
29) (a)Y. Inai, K. Tagawa, M.Yamashita, J. Am.Chem. Soc. 2000, 122, 11731-11732. (b)Y. Inai, Y. Ishida, T. Hirabayashi, J. Am. Chem. Soc. 2002, 124, 2466-2473.
30) E. Yashima, H. Goto, Y. Okamoto, Macromolecules 1999, 32, 7942-7945.
31) H. Goto, E. Yashima, J. Am. Chem. Soc. 2002, 124, 7943-7949.
32)Y. Kishimoto, M. Itou, R. Noyori, Macromolecules 1995, 28, 6662-6666.
33) (a) F. Takei, K. Onitsuka, S. Takahashi, Angew. Chem. Int. Ed. Engl. 1996 , 35, 1554-1556. (b) F. Takei, K. Onitsuka, S. Takahashi, Polymer J. 2000, 32 , 524-526.
34)P. Kamer, M.Cleij, R.Nolte,W. Drenth, J. Am. Chem. Soc. 1988, 110, 1581-1587.
35) Y. Ito, E. Ihara, M. Murakami, J. Am. Chem. Soc. 1990, 112, 6446-6447.
36) Y. Ito, Y. Kojima, M. Murakami, Tetrahedron Lett. 1993, 34, 8279-8282.
37)Y. Ito, Y.Kojima,M.Murakami,Angew.Chem. Int. Ed. Engl. 1992, 31 , 1509-11510.
38) (a) Y. Ito, T. Ohara, M. Suginome, J. Am. Chem. Soc. 1996, 118, 9188-9189. (b) Y. Ito, T. Ohara, M. Suginome, J. Am. Chem. Soc. 1998, 120, 11880-11893. (c) Y. Ito, T. Ohara, M. Suginome, Macromolecules 1998, 31 , 1697- 1699.
注:本文为提供者整理翻译的,由于知识所限,错误在所难免,敬请原谅。如有问题可以查找原文。



 沪公网安备 31010602001115号
沪公网安备 31010602001115号